
21 de noviembre de 2025
Salk Institute researchers find new mode of epigenetic targeting, showing for the first time that genetic sequences can direct new DNA methylation patterns in plants—opening new possibilities for precisely correcting epigenetic defects to improve human health and agriculture
Salk Institute researchers find new mode of epigenetic targeting, showing for the first time that genetic sequences can direct new DNA methylation patterns in plants—opening new possibilities for precisely correcting epigenetic defects to improve human health and agriculture
LA JOLLA—Todas las células de un organismo tienen la misma secuencia genética. Lo que difiere entre los tipos de células es su epigenética—etiquetas químicas colocadas meticulosamente que influyen en qué genes se expresan en cada célula. Los errores o fallos en la regulación epigenética pueden provocar graves defectos de desarrollo tanto en plantas como en animales. Esto plantea una pregunta desconcertante: si los cambios epigenéticos regulan nuestra genética, ¿qué los regula a ellos?
Científicos del Instituto Salk han utilizado células vegetales para descubrir que un tipo de etiqueta epigenética, llamada metilación del ADN, puede ser regulada por mecanismos genéticos. Este nuevo modo de direccionamiento de la metilación del ADN en plantas utiliza secuencias específicas de ADN para indicar a la maquinaria de metilación dónde acoplarse. Antes de este estudio, los científicos solo entendían cómo la metilación del ADN era regulada por otras características epigenéticas, por lo que el descubrimiento de que genético las características también pueden guiar los patrones de metilación del ADN es un cambio de paradigma importante.
Estos hallazgos podrían informar futuras estrategias de ingeniería epigenética dirigidas a generar patrones de metilación predichos para reparar o mejorar la función celular, con muchas aplicaciones potenciales en medicina y agricultura.

“En plantas y animales, patrones incorrectos de metilación del ADN pueden causar defectos de desarrollo, y en mamíferos, eso puede llevar a numerosas enfermedades, incluido el cáncer”, dice el autor principal. Julie Law, PhD, bioquímica y profesora asociada en Salk. “Esto hace que sea muy importante para nosotros entender cómo la metilación del ADN se dirige a los lugares correctos en los tejidos y etapas de desarrollo correctos. Nuestro trabajo responde a una pregunta de larga data sobre cómo se generan nuevos patrones de metilación durante el desarrollo de las plantas, que es el primer paso para pensar en la ingeniería de patrones de metilación del ADN para mejorar la aptitud celular”.”
El estudio se publicó en Naturaleza y Biología Celular el 21 de noviembre de 2025, y fue financiado tanto por subvenciones federales de investigación de los Institutos Nacionales de Salud como por filantropía privada.
¿Qué es la epigenética?
Las instrucciones celulares están escritas en un idioma de cuatro letras: A, T, C y G, que se unen para formar largas hebras de ADN. Estas hebras largas y rebeldes de ADN se enrollan luego alrededor de proteínas llamadas histonas y se empaquetan en cromatina, condensando y organizando las hebras para un fácil almacenamiento y acceso. El epigenoma es una capa de etiquetas y modificaciones realizadas encima de todo eso. Estos cambios determinan qué genes se expresan y cuáles no, sin alterar el código base en sí, lo que permite flexibilidad en la identidad y el comportamiento celular.
Una etiqueta epigenética prominente es la metilación del ADN, en la cual un grupo metilo se adhiere a letras “C” específicas dentro del código del ADN. Estas etiquetas de metilación del ADN señalan que el ADN subyacente debe ser “apagado”, un proceso llamado “silenciamiento”. Este proceso es importante no solo para regular la expresión génica, sino también para silenciar la expresión de elementos genéticos especiales, llamados transposones. Si se expresan, los transposones pueden moverse dentro del genoma, lo que resulta en inestabilidad genómica y una menor aptitud del organismo.
Comprender cómo, cuándo y por qué se generan patrones específicos de metilación del ADN en cada tipo de célula es crucial para explicar el desarrollo biológico y tratar enfermedades que involucran disfunción epigenética.
“Hemos aprendido mucho sobre cómo una etiqueta epigenética puede mantenerse después de que se ha establecido”, explica Law. “Pero la diversidad celular no proviene de patrones sostenidos; proviene de." Nuevo patrones, y hay mucho que aún no sabemos sobre qué crea un nuevo patrón epigenético. Este trabajo está llenando esa brecha entre saber que existe diversidad epigenética y comprender cómo se genera.”
¿Por qué estudiar epigenética en plantas?
Arabidopsis thaliana es una pequeña maleza con flores que ha servido como la planta de laboratorio básica durante décadas. Arabidopsis tolera mejor las interrupciones experimentales en las modificaciones epigenéticas que las células humanas u otras células animales, por lo que es un gran recurso para investigar preguntas fundamentales sobre la epigenética.
En Arabidopsis, los patrones de metilación del ADN son regulados por una familia de cuatro proteínas llamadas CLASSYs. Cada CLASSY es responsable de reclutar la maquinaria de metilación del ADN a diferentes ubicaciones dentro del genoma. Pero antes de este estudio de Salk, los científicos no tenían claro cómo CLASSY3 medió esta selección. ¿Qué lo hizo elegir un conjunto de objetivos genómicos sobre otros?
¿Cómo comienzan los cambios epigenéticos?
Hasta este punto, los científicos solo habían observado cómo los eventos de metilación del ADN eran dirigidos por otras características epigenéticas. Por ejemplo, si una sección de ADN ya había sido metilada para suprimir la expresión génica en esa región, los científicos entendían cómo esta metilación podía restablecerse en la misma ubicación después de la división celular.
Estos mecanismos de autorrefuerzo son especialmente importantes para mantener los patrones epigenéticos durante la vida de un organismo. Por ejemplo, cuando una célula de la piel envejece y se divide en dos nuevas células cutáneas, no querrás que surja un patrón epigenético completamente nuevo y que reprograme repentinamente esas células cutáneas en células cancerosas.
Pero, ¿qué pasa en los casos en los que tú hacer ¿Quieres que el patrón epigenético cambie, como durante el desarrollo o en respuesta a un estrés ambiental? ¿Cómo modifica una célula vegetal su epigenética para crecer, responder y recuperarse?
“¿Cómo estos patrones comenzar?” pregunta el primer autor Guanghui Xu, PhD, investigador postdoctoral en el laboratorio de Law. “Queríamos saber qué estaba regulando las vías epigenéticas para crear nuevos patrones de metilación del ADN durante el desarrollo, la regeneración y la reproducción de las plantas”.”
Un cambio de paradigma en la metilación del ADN de las plantas
Para investigar cómo se originan estos patrones de metilación del ADN, los investigadores observaron Arabidopsis tejidos reproductivos. Utilizando una pantalla genética directa, descubrieron un nuevo modo de direccionamiento de la metilación del ADN que se basa en secuencias de ADN en lugar de características epigenéticas.
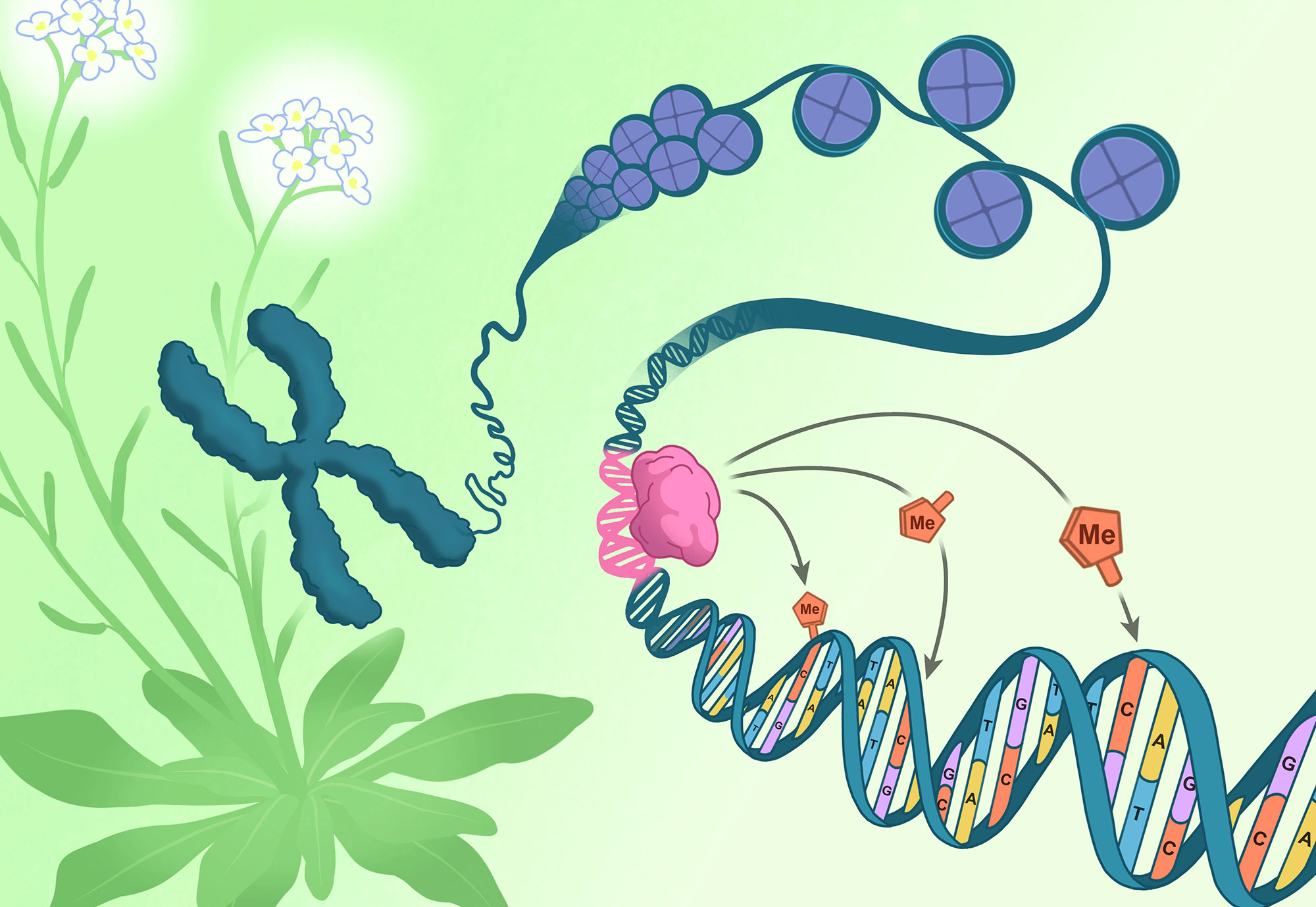
Se descubrieron varias proteínas, a las que el equipo denominó “RIMs”, que actúan junto con CLASSY3 para establecer la metilación del ADN en objetivos genómicos específicos en los tejidos reproductivos de las plantas. Estas RIMs son un subconjunto de una gran clase de proteínas llamadas factores de transcripción MERISTEMO REPRODUCTIVO (REM). Este fue un descubrimiento sorprendente, ya que relacionó la identificación de CLASSY3 con secuencias de ADN específicas. Cuando los científicos alteraron estos tramos de ADN, toda la vía de metilación falló.
El estudio identifica tramos indispensables de ADN donde los RIMs se acoplan, después de lo cual pueden dirigirse a la maquinaria de metilación del ADN para afectar secuencias de ADN vecinas. Como resultado de esta actividad de direccionamiento, los investigadores demostraron que se generan patrones únicos de metilación en los tejidos reproductivos que expresan diferentes combinaciones de RIMs. Esta es la primera vez que los científicos identifican una secuencia genética que puede impulsar el proceso epigenético de metilación del ADN en plantas. Dado que hay muchos genes REM en Arabidopsis, el equipo espera que miembros adicionales de la familia estén vinculados a la metilación del ADN, expandiendo sus roles en el control de la regulación epigenética.
Otro Naturaleza y Biología Celular un estudio dirigido por Steven Jacobsen, PhD, de la UC Los Ángeles utilizó genética inversa para identificar varios genes REM involucrados en la regulación de la metilación del ADN a través de secuencias específicas de ADN, lo que respalda aún más el papel de la información genética en la guía de los procesos epigenéticos.
“Este hallazgo representa un cambio de paradigma en la visión del campo sobre cómo se regula la metilación en las plantas”, dice Law. “Todo el trabajo anterior apuntaba a modificaciones epigenéticas preexistentes como punto de partida para dirigir la metilación, lo que no explicaba cómo podían surgir nuevos patrones de metilación. Ahora sabemos que el propio ADN también puede instruir nuevos patrones de metilación”.”
Armados con esta nueva evidencia de que las características genéticas pueden instruir cambios epigenéticos, los investigadores tienen una gran cantidad de preguntas adicionales por explorar, incluyendo cuán extendido está este nuevo modo de direccionamiento durante el desarrollo de las plantas y cómo se puede aprovechar para diseñar patrones novedosos de metilación del ADN. La capacidad de usar secuencias de ADN para dirigir la metilación tiene amplias implicaciones para la agricultura y la salud humana, ya que permitiría corregir defectos epigenéticos con un alto grado de precisión.
Otros autores incluyen a Yuhan Chen, Laura M. Martins, En Li, Fuxi Wang, Tulio Magana y Junlin Ruan del Salk.
El trabajo fue financiado por los National Institutes of Health (GM112966, P30 CA01495, P30 AG068635), el Paul F. Glenn Center for Biology of Aging Research del Salk, la beca postdoctoral Salk Pioneer, la Chapman Foundation y el Helmsley Charitable Trust.
DOI: 10.1038/s41556-025-01808-5
DIARIO
Naturaleza y Biología Celular
AUTORES
Guanghui Xu, Yuhan Chen, Laura M. Martins, En Li, Fuxi Wang, Tulio Magana, Junlin Ruan, and Julie A. Law
Oficina de Comunicaciones
Tel.: (858) 453-4100
press@salk.edu
El Instituto Salk es un centro de investigación independiente y sin fines de lucro fundado en 1960 por Jonas Salk, creador de la primera vacuna segura y eficaz contra la poliomielitis. La misión del Instituto es impulsar una investigación fundamental, colaborativa y audaz que aborde los retos más acuciantes de la sociedad, entre ellos el cáncer, la enfermedad de Alzheimer y la vulnerabilidad agrícola. Esta ciencia fundamental sustenta todos los esfuerzos traslacionales, generando conocimientos que permiten el desarrollo de nuevos medicamentos e innovaciones en todo el mundo.