
21. November 2025
Salk Institute researchers find new mode of epigenetic targeting, showing for the first time that genetic sequences can direct new DNA methylation patterns in plants—opening new possibilities for precisely correcting epigenetic defects to improve human health and agriculture
Salk Institute researchers find new mode of epigenetic targeting, showing for the first time that genetic sequences can direct new DNA methylation patterns in plants—opening new possibilities for precisely correcting epigenetic defects to improve human health and agriculture
LA JOLLA – Alle Zellen eines Organismus haben exakt die gleiche genetische Sequenz. Was sich zwischen den Zelltypen unterscheidet, ist ihre Epigenetik– akribisch platzierte chemische Markierungen, die beeinflussen, welche Gene in jeder Zelle exprimiert werden. Fehler oder Versagen der epigenetischen Regulation können sowohl bei Pflanzen als auch bei Tieren zu schweren Entwicklungsstörungen führen. Dies wirft eine verwirrende Frage auf: Wenn epigenetische Veränderungen unsere Genetik regulieren, was reguliert sie dann?
Scientists at the Salk Institute have now used plant cells to discover that a type of epigenetic tag, called DNA methylation, can be regulated by genetic mechanisms. This new mode of plant DNA methylation targeting uses specific DNA sequences to tell the methylation machinery where to dock. Prior to this study, scientists had understood only how DNA methylation was regulated by other epigenetic features, so the discovery that genetic features can also guide DNA methylation patterns is a major paradigm shift.
These findings could inform future epigenetic engineering strategies aimed at generating methylation patterns predicted to repair or enhance cell function, with many potential applications in medicine and agriculture.

“In plants and animals, incorrect patterns of DNA methylation can cause developmental defects, and in mammals, that can lead to numerous diseases—including cancer,” says senior author Julie Law, PhD, a biochemist and associate professor at Salk. “This makes it very important for us to understand how DNA methylation is targeted to the correct locations in the correct tissues and developmental stages. Our work answers a long-standing question about how new patterns of methylation are generated during plant development, which is the first step in thinking about engineering DNA methylation patterns to improve cellular fitness.”
The study was published in Nature Cell Biology on November 21, 2025, and was funded by both federal research grants from the National Institutes of Health and private philanthropy.
What is epigenetics?
Cellular instructions are written in a four-letter language—A, T, C, and G—which string together to form long strands of DNA. These long, unruly stretches of DNA are then spooled around proteins called histones and packaged into chromatin—condensing and organizing the strands for easy storage and access. The epigenome is a layer of tags and modifications made on top of all that. These changes determine which genes are and aren’t expressed without altering the base code itself, allowing for flexibility in cellular identity and behavior.
One prominent epigenetic tag is DNA methylation, in which a methyl group is tacked onto specific “C” letters within the DNA code. These DNA methylation tags signal for the underlying DNA to be turned “off”—a process called “silencing.” This process is important not only for regulating gene expression, but also for silencing the expression of special genetic elements, called transposons. If expressed, transposons can move within the genome, resulting in genome instability and reduced organismal fitness.
Understanding how, when, and why specific DNA methylation patterns are generated in each cell type is crucial for explaining biological development and treating diseases that involve epigenetic dysfunction.
“We’ve learned a lot about how an epigenetic tag can be maintained after it’s been established,” explains Law. “But cellular diversity doesn’t come from sustained patterns; it comes from new patterns, and there’s a lot we still don’t know about what creates a new epigenetic pattern. This work is filling that gap between knowing epigenetic diversity exists and understanding how it is generated.”
Why study epigenetics in plants?
Arabidopsis thaliana is a small flowering weed that has served as the staple laboratory plant for decades. Arabidopsis tolerates experimental disruptions in epigenetic modifications better than human or other animal cells can, so it’s a great resource for investigating fundamental questions about epigenetics.
In Arabidopsis, DNA methylation patterns are regulated by a family of four proteins called the CLASSYs. Each CLASSY is responsible for recruiting the DNA methylation machinery to different locations within the genome. But prior to this Salk study, scientists were unclear how CLASSY3 mediated this targeting. What made it choose one set of genomic targets over others?
How do epigenetic changes start?
Up until this point, scientists had only observed DNA methylation events being targeted by other epigenetic features. For example, if a section of DNA had already been methylated to suppress gene expression in that region, scientists understood how this methylation could be reestablished at that same location after cell division.
These self-reinforcing mechanisms are especially important for maintaining epigenetic patterns during an organism’s life. For example, when an aging skin cell is dividing into two new skin cells, you wouldn’t want an entirely new epigenetic pattern to emerge and suddenly reprogram those skin cells into cancer cells.
But what about cases where you do want the epigenetic pattern to change—like during development or in response to an environmental stress? How does a plant cell modify its epigenetics to grow, respond, and recover?
“How do these patterns start?” asks first author Guanghui Xu, PhD, a postdoctoral researcher in Law’s lab. “We wanted to know what was regulating epigenetic pathways to create new DNA methylation patterns during plant development, regeneration, and reproduction.”
A paradigm shift in plant DNA methylation
To investigate how these DNA methylation patterns originate, the researchers looked at Arabidopsis reproductive tissues. Using a forward genetic screen, they discovered a new mode of DNA methylation targeting that relies on DNA sequences rather than epigenetic features.
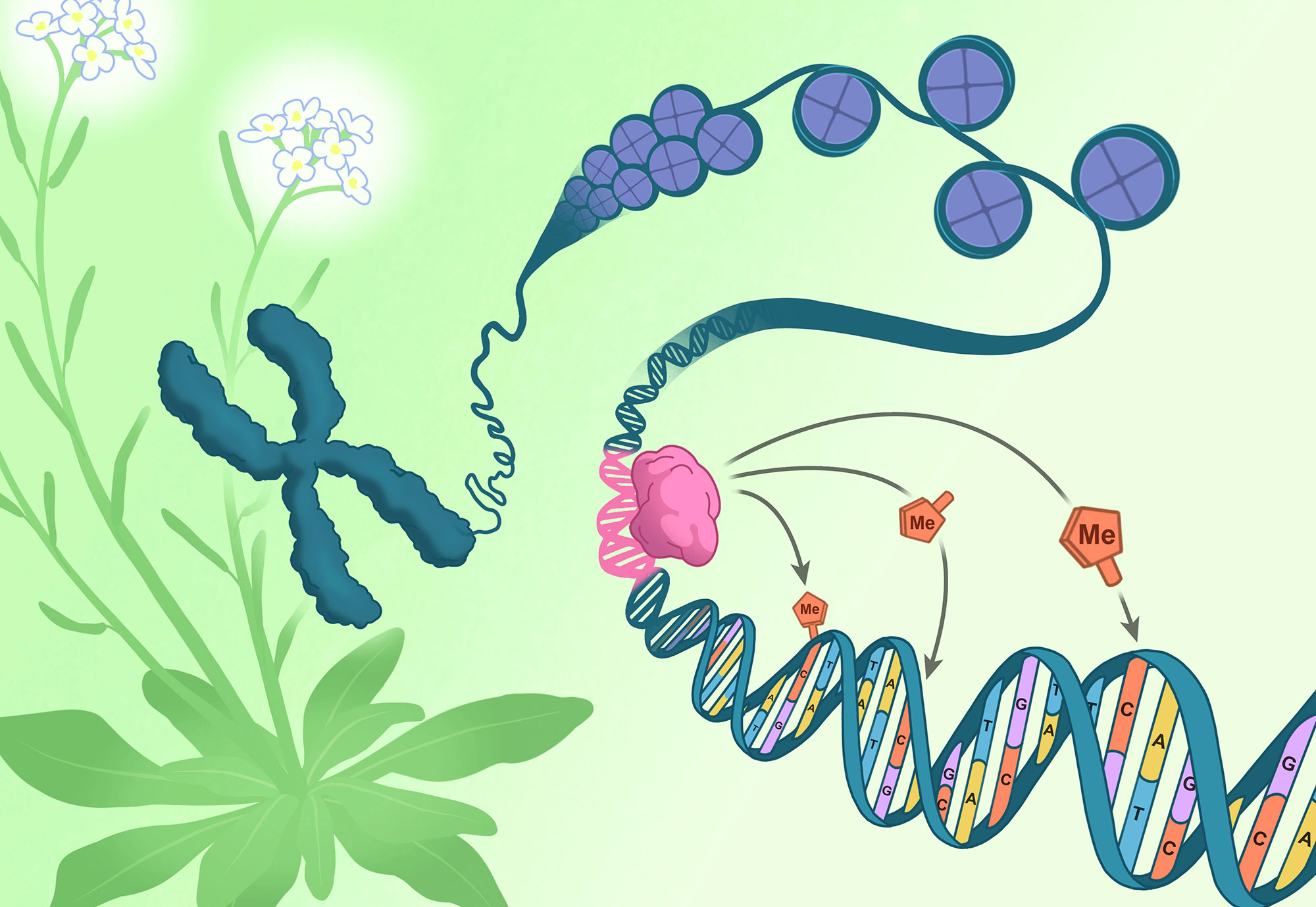
Several proteins, which the team named “RIMs,” were found to act with CLASSY3 to establish DNA methylation at specific genomic targets in plant reproductive tissues. These RIMs are a subset of a large protein class called REPRODUCTIVE MERISTEM (REM) transcription factors. This was a surprising discovery, as it linked CLASSY3 targeting to specific DNA sequences. When the scientists disrupted these stretches of DNA, the entire methylation pathway failed.
The study identifies indispensable stretches of DNA where RIMs dock, after which they can target the DNA methylation machinery to affect neighboring DNA sequences. As a result of this targeting activity, the researchers demonstrated that unique patterns of methylation are generated in reproductive tissues that express different combinations of RIMs. This is the first time scientists have identified a genetic sequence that can drive the epigenetic process of DNA methylation in plants. As there are many REM genes in Arabidopsis, the team expects that additional family members will be linked to DNA methylation, expanding their roles in controlling epigenetic regulation.
Another Nature Cell Biology study led by Steven Jacobsen, PhD, at UC Los Angeles used reverse genetics to identify several REM genes involved in regulating DNA methylation through specific DNA sequences—further supporting the role of genetic information in guiding epigenetic processes.
“This finding represents a paradigm shift in the field’s view of how methylation is regulated in plants,” says Law. “All previous work pointed to pre-existing epigenetic modifications as the starting place for targeting methylation, which didn’t explain how novel methylation patterns could arise. Now we know the DNA itself can instruct new methylation patterns, too.”
Armed with this new evidence that genetic features can instruct epigenetic changes, researchers have a host of additional questions to explore, including how widespread this new targeting mode is during plant development and how it can be leveraged to engineer novel patterns of DNA methylation. The ability to use DNA sequences to target methylation has broad implications for agriculture and human health, as it would allow epigenetic defects to be corrected with a high degree of precision.
Other authors include Yuhan Chen, Laura M. Martins, En Li, Fuxi Wang, Tulio Magana, and Junlin Ruan of Salk.
The work was supported by the National Institutes of Health (GM112966, P30 CA01495, P30 AG068635), Salk’s Paul F. Glenn Center for Biology of Aging Research, the Salk Pioneer postdoctoral fellowship, Chapman Foundation, and Helmsley Charitable Trust.
DOI: 10.1038/s41556-025-01808-5
JOURNAL
Nature Cell Biology
AUTOREN
Guanghui Xu, Yuhan Chen, Laura M. Martins, En Li, Fuxi Wang, Tulio Magana, Junlin Ruan, and Julie A. Law
Büro für Kommunikation
Telefon: (858) 453-4100
press@salk.edu
Das Salk Institute ist ein unabhängiges, gemeinnütziges Forschungsinstitut, das 1960 von Jonas Salk, dem Entwickler des ersten sicheren und wirksamen Polio-Impfstoffs, gegründet wurde. Die Aufgabe des Instituts besteht darin, grundlegende, kooperative und risikofreudige Forschung voranzutreiben, die sich mit den dringendsten Herausforderungen der Gesellschaft befasst, darunter Krebs, Alzheimer und die Gefährdung der Landwirtschaft. Diese Grundlagenforschung bildet die Basis für alle translationalen Bemühungen und führt zu Erkenntnissen, die neue Medikamente und Innovationen weltweit ermöglichen.