
26 de Junho de 2017
Os cientistas da Salk aprimoraram uma abordagem clássica para mapear as interações entre proteínas
Os cientistas da Salk aprimoraram uma abordagem clássica para mapear as interações entre proteínas
LA JOLLA—Cientistas do Salk desenvolveram uma nova técnica de alto rendimento para determinar quais proteínas em uma célula interagem umas com as outras. O mapeamento dessa rede de interações, ou “interactoma”, foi lento no passado porque o número de interações que podiam ser testadas de uma só vez era limitado. A nova abordagem, publicada em 26 de junho na Nature Methods, permite que os pesquisadores testem milhões de relações entre milhares de proteínas em um único experimento.
Clique aqui para uma imagem de alta resolução
Crédito: Salk Institute
“O poder dessa nova abordagem está na capacidade que agora temos de ampliá-la”, diz o autor sênior José Ecker, professor e diretor do Laboratório de Análise Genômica de Salk e investigador do Howard Hughes Medical Institute. “Este ensaio tem o potencial de começar a abordar questões sobre interações biológicas fundamentais que não conseguimos abordar antes”.
O interactoma de uma célula, como um mapa de redes sociais, permite aos cientistas ver quem está trabalhando com quem no mundo das proteínas. Isso os ajuda a descobrir os papéis de diferentes proteínas e a juntar os diferentes atores nas vias e processos moleculares. Se uma proteína recém-descoberta interage com muitas outras proteínas envolvidas no metabolismo celular, por exemplo, os pesquisadores podem deduzir que esse é um papel provável para a nova proteína e potencialmente direcioná-la para tratamentos relacionados à disfunção metabólica.
Até agora, os pesquisadores normalmente confiavam em ensaios padrão de dois híbridos de levedura (Y2H) de alto rendimento para determinar as interações entre as proteínas. O sistema requer o uso de uma única proteína conhecida – conhecida como “isca” – para rastrear um conjunto de proteínas “presas”. Mas encontrar todas as interações entre, por exemplo, 1,000 proteínas, exigiria 1000 experimentos separados para rastrear uma vez os parceiros de interação de cada isca.
“As tecnologias atuais exigem essencialmente que as interações detectadas na triagem primária sejam retestadas individualmente”, diz Shelly Trigg, bolsista de pesquisa de pós-graduação da NSF no University of California, San Diego, no laboratório Ecker, e primeiro autor do novo artigo. “Isso pode não ser mais necessário com a profundidade de triagem que essa abordagem alcança.”
Em seu novo método, Ecker, Trigg e seus colegas acrescentaram uma reviravolta ao ensaio Y2H padrão para uma maneira muito mais eficaz de medir o interactoma. Os genes para duas proteínas, cada uma em seu próprio círculo de DNA, são adicionados à mesma célula. Se as proteínas de interesse interagem dentro da célula, um gene chamado Cre é ativado. Quando ativado, o Cre une fisicamente os dois círculos individuais de DNA, emparelhando assim os genes das proteínas que interagem para que a equipe possa encontrá-los facilmente por meio do sequenciamento. A equipe pode gerar uma enorme biblioteca de células de levedura – cada uma contendo diferentes pares de proteínas, introduzindo combinações aleatórias de genes no DNA circular chamados plasmídeos. Quando as células são positivas para uma interação de proteína, os pesquisadores podem usar o sequenciamento genético para descobrir quais são as duas proteínas que interagem, usando novas tecnologias de sequenciamento de DNA de alto rendimento semelhantes às usadas para o sequenciamento do genoma humano. Dessa forma, eles não estão mais limitados a testar uma proteína “isca” por vez, mas podem testar as interações entre todas as proteínas em uma biblioteca de uma só vez.

Clique aqui para uma imagem de alta resolução.
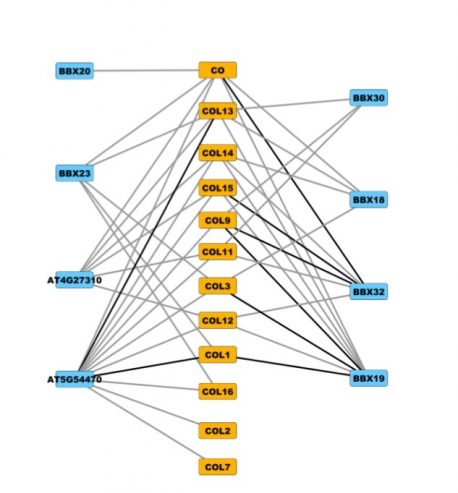
O grupo de Ecker testou o novo método, apelidado de CrY2H-seq, em todos os fatores de transcrição – uma grande classe de proteínas – na planta Arabidopsis.
“Quando você pega 1,800 proteínas e testa as interações entre elas, são quase 4 milhões de combinações”, diz Ecker. “Fizemos isso dez vezes em questão de um mês.”
Eles revelaram mais de 8,000 interações entre as proteínas testadas, dando-lhes uma nova visão sobre qual Arabidopsis fatores de transcrição interagem uns com os outros. Os dados, dizem eles, ajudam a responder questões de longa data sobre se certos grupos de fatores de transcrição têm funções definidas. Alguns dos fatores de transcrição mal compreendidos, eles descobriram, interagem com fatores mais bem compreendidos que regulam a resposta da planta à auxina, um hormônio envolvido na coordenação do crescimento da planta.
No futuro, o método pode ser ampliado para testar conjuntos maiores de proteínas – as células humanas, por exemplo, contêm cerca de 20,000 proteínas diferentes. Esse método mais fácil e rápido de determinar todo o interactoma de uma célula também abre a possibilidade de estudar como o interactoma muda sob diferentes condições - um experimento que nunca foi possível no passado.
Outros pesquisadores do estudo foram Renee Garza, Andrew MacWilliams, Joseph Nery, Anna Bartlett, Rosa Castanon, Adeline Goubil, Joseph Feeney, Ronan O'Malley, Shao-shan Carol Huang, Zhuzhu Zhang e Mary Galli do Salk Institute.
O trabalho e os pesquisadores envolvidos foram apoiados por bolsas do Departamento de Energia dos EUA, Programa de bolsas de pós-graduação da National Science Foundation, Instituto Médico Howard Hughes e Fundação Mary K. Chapman.
JORNAL
Nature Methods
IMERSÃO DE INGLÊS
CrY2H-seq: um ensaio massivamente multiplexado para mapeamento interativo de cobertura profunda
AUTORES
Shelly A Trigg, Renee M Garza, Andrew MacWilliams, Joseph R Nery, Anna Bartlett, Rosa Castanon, Adeline Goubil, Joseph Feeney, Ronan O'Malley, Shao-shan C Huang, Zhuzhu Z Zhang, Mary Galli e Joseph R Ecker
CAPA DA REVISTA
Um método de dois híbridos de levedura massivamente multiplexados, CrY2H-seq, permite o mapeamento de cobertura profunda do Arabidopsis interativo. Capa preparada por Erin Dewalt, com base no design e arte de Shelly Trigg, Lisa Servilio e Jamie Simon no The Salk Institute for Biological Studies e por Austin Trigg na Austin Trigg Photography.
Escritório de Comunicações
Tel: (858) 453-4100
press@salk.edu
O Instituto Salk é um instituto de pesquisa independente e sem fins lucrativos, fundado em 1960 por Jonas Salk, criador da primeira vacina segura e eficaz contra a poliomielite. A missão do Instituto é impulsionar pesquisas fundamentais, colaborativas e inovadoras que abordem os desafios mais urgentes da sociedade, incluindo câncer, doença de Alzheimer e vulnerabilidade agrícola. Essa ciência fundamental sustenta todos os esforços translacionais, gerando conhecimento que possibilita o desenvolvimento de novos medicamentos e inovações em todo o mundo.